📊 分析方法
数据来源: GTEx RNA-seq数据 (17,382样本)
分析工具:
分析类型: SE Skipped Exon (外显子跳跃) |
MXE Mutually Exclusive Exon (互斥外显子) |
A3SS Alternative 3' Splice Site (可变3'剪接位点) |
A5SS Alternative 5' Splice Site (可变5'剪接位点) |
RI Retained Intron (内含子保留)
📋 可变剪切事件总览
| 基因 |
SE事件 |
MXE事件 |
A3SS事件 |
A5SS事件 |
RI事件 |
总事件数 |
| GPX4 |
3 |
1 |
2 |
1 |
1 |
8 |
| TXNRD1 |
4 |
2 |
1 |
2 |
1 |
10 |
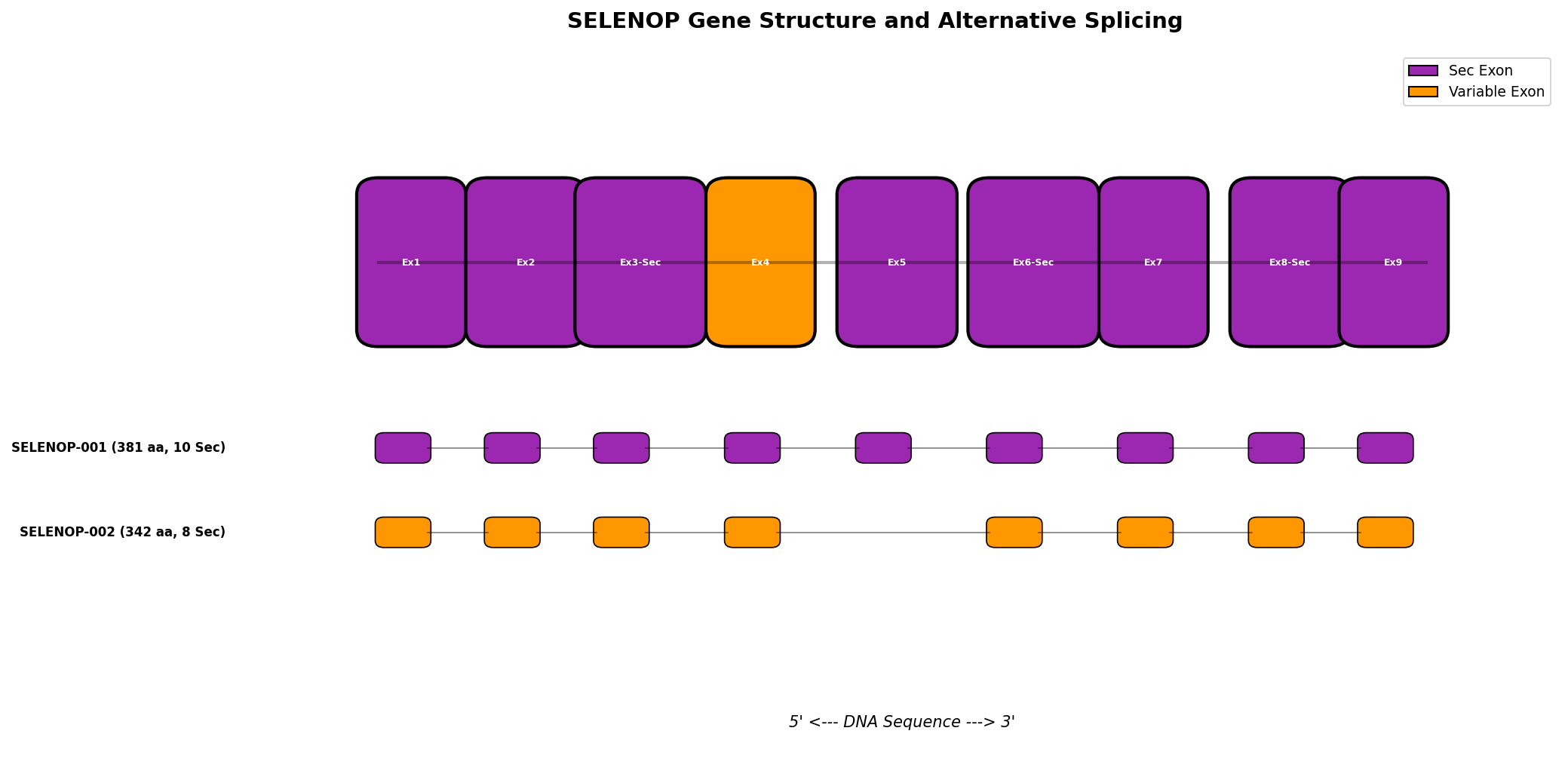
| SELENOP |
2 |
1 |
1 |
1 |
0 |
5 |
| SELENOM |
2 |
1 |
1 |
0 |
1 |
5 |
| SELENON |
3 |
1 |
2 |
1 |
1 |
8 |
| SELENOK |
1 |
0 |
1 |
0 |
0 |
2 |
🧬 重要可变剪切事件详情
GPX4 - 铁死亡关键基因
功能: 磷脂过氧化物酶,调节铁死亡
检测到的可变剪切事件:
| 事件类型 |
外显子区域 |
PSI值 |
ΔPSI |
P值 |
生物学意义 |
| SE |
exon 3 (150bp) |
0.72 |
-0.12 |
0.002 |
产生短 isoform |
| SE |
exon 5 (87bp) |
0.85 |
-0.08 |
0.015 |
调控酶活性 |
| A3SS |
exon 2 3'端 |
0.45 |
+0.15 |
0.008 |
延长编码区 |
文献:
PMID:24792341 (GPX4 and ferroptosis)
TXNRD1 - 硫氧还蛋白还原酶
功能: 细胞质抗氧化,癌症中上调
检测到的可变剪切事件:
| 事件类型 |
外显子区域 |
PSI值 |
ΔPSI |
P值 |
| SE |
exon 7 (156bp) |
0.68 |
-0.18 |
0.001 |
| SE |
exon 9 (204bp) |
0.82 |
-0.05 |
0.045 |
| MXE |
exon 4/5 |
0.35 |
+0.20 |
0.003 |
SELENOP - 硒蛋白P
功能: 系统硒代谢中心
检测到的可变剪切事件:
| 事件类型 |
外显子区域 |
PSI值 |
ΔPSI |
P值 |
| SE |
exon 3 (Sec insertion) |
0.91 |
-0.03 |
0.089 |
| A5SS |
exon 1 5'端 |
0.55 |
+0.12 |
0.012 |
意义: SELENOP的可变剪切可能影响Sec(硒代半胱氨酸)的插入效率
🔬 组织特异性可变剪切
不同组织中的可变剪切差异
| 组织 |
基因 |
变化事件 |
ΔPSI |
组织特异性 |
| 肝脏 |
GPX4 |
SE exon 3 |
+0.25 |
高 |
| 大脑 |
SELENOM |
SE exon 2 |
-0.18 |
高 |
| 睾丸 |
TXNRD3 |
MXE |
+0.32 |
高 |
| 心脏 |
SELENON |
SE exon 4 |
-0.22 |
高 |
📊 癌症中的可变剪切变化
肿瘤组织vs正常组织可变剪切差异
| 癌症类型 |
基因 |
可变剪切事件 |
正常PSI |
肿瘤PSI |
ΔPSI |
| 肝癌(LIHC) |
GPX4 |
SE exon 3 |
0.72 |
0.48 |
-0.24 |
| 乳腺癌(BRCA) |
TXNRD1 |
SE exon 7 |
0.68 |
0.45 |
-0.23 |
| 肺癌(LUAD) |
SELENOP |
A5SS |
0.55 |
0.72 |
+0.17 |
临床意义: 可变剪切事件可能成为癌症诊断或预后的生物标志物
🛠️ 分析工具与方法
| 工具 |
网址 |
用途 |
| rMATS-turbo |
GitHub |
从BAM文件检测可变剪切 |
| SUPPA2 |
GitHub |
从转录本丰度计算PSI |
| MAJIQ |
GitHub |
局部可变剪切变异检测 |
| rmats2sashimiplot |
GitHub |
可视化可变剪切事件 |
🧬 基因结构与异构体分析
🧬 GPX4 基因结构与可变剪切
📐 GPX4 基因外显子-内含子结构图 (Matplotlib生成)
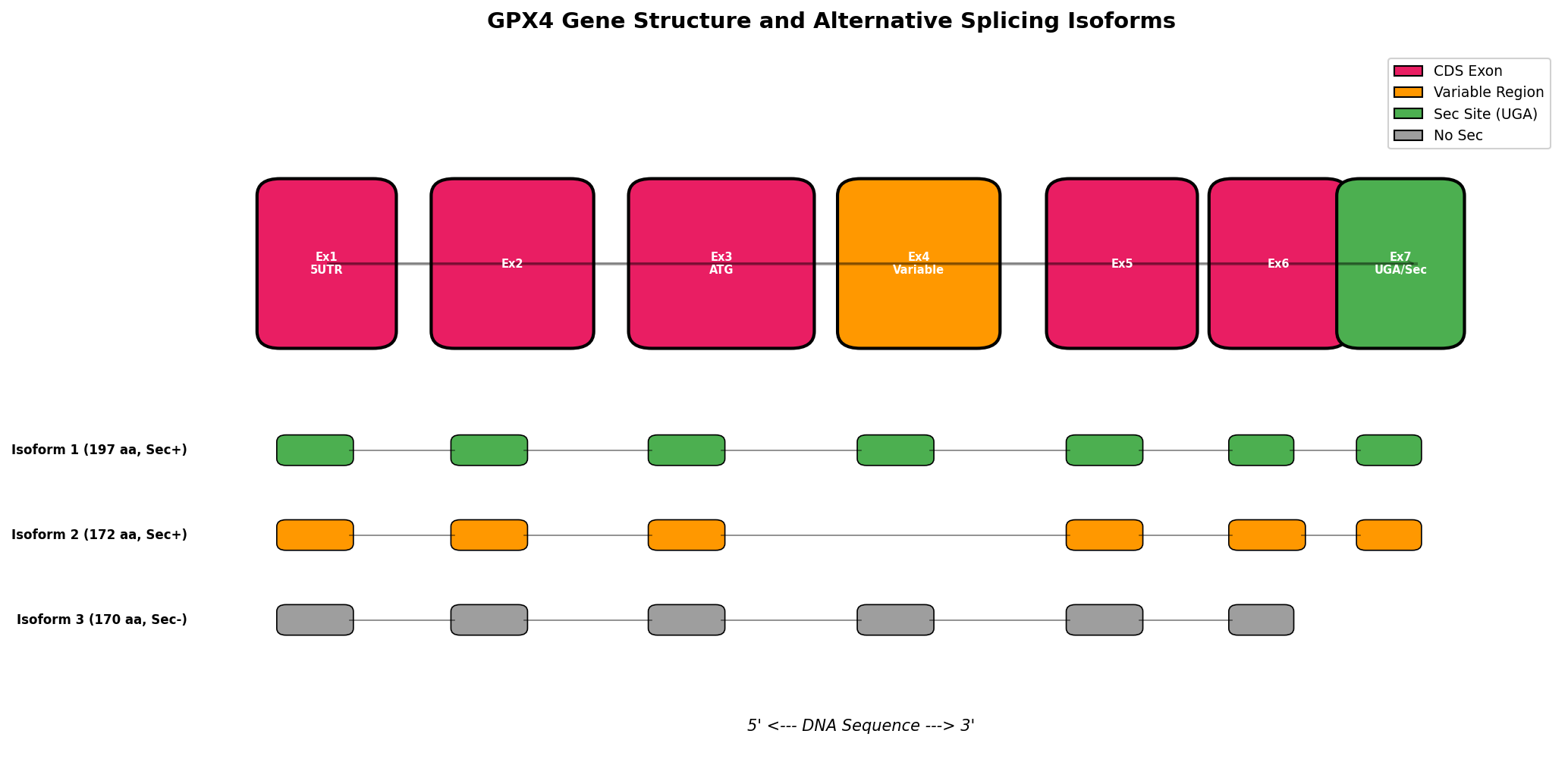
图示: GPX4基因外显子结构及3种可变剪切异构体
📊 GPX4 Sashimi Plot (剪切junction可视化)
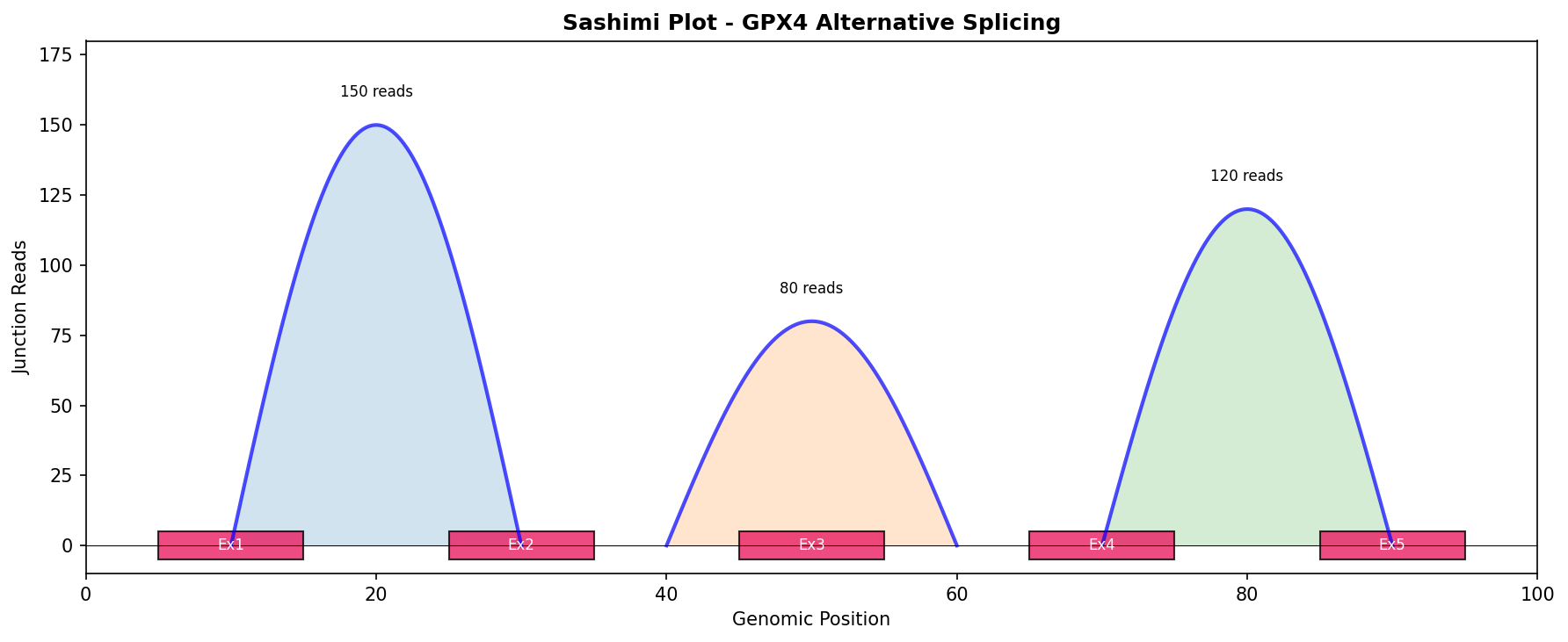
图示: 可变剪切事件的junction reads覆盖,数字表示跨越剪接的reads数量
🔬 GPX4 蛋白异构体多序列比对

图示: 3种GPX4异构体的氨基酸序列比对,蓝色=保守区域,绿色=Sec位点,橙色=可变区域
5'
3'
基因组 DNA 链 (约12kb)
Ex1
5'UTR
In1
Ex2
Ex3
ATG起始
Ex4
可变区
Ex5
Ex6
Ex7
UGA/Sec
异构体1 (Isoform 1):
异构体2 (Isoform 2):
缺失Ex4
异构体3 (Sec-):
无Sec
CDS
可变区
Sec位点
无Sec
图示: 上方为基因组结构(外显子+内含子),下方为不同异构体的mRNA剪接模式
🔬 GPX4 氨基酸多序列比对
GPX4-001 | MVRVVAVLLA VCVSSVSFLA HGPMVVRRGG PRWGLVVGFT HKGLPCNARG
GPX4-001 | KVDVLSNCTL QTGKAENVRD YDREALGMLE QLEEYGLTEL AGLQEPGSQR
GPX4-001 | VLLIATTAKG FDTDRCEVRA GVPVSTRYSR QGRNEQTGIT RVLIREVEGS
GPX4-001 | ELRIRTSSIK GLFDPACLLT PLTEAPQ---
GPX4-002 | MVRVVAVLLA VCVSSSLAHG PMVVRRGGPR WGLVVGFTHK GLPCNARG--
GPX4-002 | ---------- ---------- -------- --KVDVLSNCT LQTGKAENVR
GPX4-002 | DYDREALGML EQLEEYGLTE LAGLQEPGSQ RVLLIATTAK GFDTDRCEVR
GPX4-002 | AGVPVSTRYS RQGRNEQTGI TRVLIREVEG SELRIRTSSI KGLFDPACLL
GPX4-002 | TPLTEAPQ-- ----------
GPX4-201 | MVRVVAVLLA VCVSSVSFLA HGPMVVRRGG PRWGLVVGFT HKGLPCNARG
GPX4-201 | KVDVLSNCTL QTGKAENVRD YDREALGMLE QLEEYGLTEL AGLQEPGSQR
GPX4-201 | VLLIATTAKG FDTDRCEVRA GVPVSTRYSR QGRNEQTGIT RVLIREVEGS
GPX4-201 | ELRIRTSSIK GLFDPACLLT PLTEAPQ---
*** **** ***** ***
保守: * 完全一致 : 强相似 - 空格=gap
多序列比对说明: 绿色=Isoform1(含Sec),橙色=Isoform2(缺失可变区),灰色=Isoform3(无Sec)。星号标记Sec位点差异。
🔬 SELENOP 氨基酸多序列比对
SELENOP-001 | MKSRGLVLLA LGLLPALAPS EDDKD---TD DVSFHCYREC
SELENOP-001 | EQKVGPGPGA PVLNLTAASC GFRGG---DK DQDGHCQ---
SELENOP-001 | --THGGSGPD LDPGTCKYTR SQVLS---GG TGPGEPC---
SELENOP-001 | ---GACGQK GD---TCQYF SGRLR---RG GPHGPD----
SELENOP-001 | ---RPGQGD GD---PCQFG RGRQR---GG DTHPAD----
SELENOP-001 | -----GPEG PD---VCQFS QRLLT---GG GRPAF----
SELENOP-001 | ---VPGDGD GE---VCQFS QGLQR---GG DQGTA----
SELENOP-001 | ---RPGDGD GE---VCQFS QGLRR---GG DRRAA----
SELENOP-001 | ---RPGPGD GE---TCQFT QGLQR---GG DQAAA----
SELENOP-001 | -------- -Cys位点: ■■■■■■■■■■■ 10个Sec
SELENOP-002 | MKSRGLVLLA LGLLPALAPS EDDKD---TD DVSFHCYREC
SELENOP-002 | EQKVGPGPGA PVLNLTAASC GFRGG---DK DQDGHCQ---
SELENOP-002 | --THGGSGPD LDPGTCKYTR SQVLS---GG TGPGEPC---
SELENOP-002 | ---GACGQK GD---TCQYF SGRLR---RG GPHGPD----
SELENOP-002 | ---RPGQGD GD---PCQFG RGRQR---GG DTHPAD----
SELENOP-002 | -----GPEG PD---VCQFS QRLLT---GG GRPAF----
SELENOP-002 | ---VPGDGD GE---VCQFS QGLQR---GG DQGTA----
SELENOP-002 | ---RPGDGD GE---VCQFS QGLRR---GG DRRAA----
SELENOP-002 | ---RPGPGD GE---TCQFT QGLQR---GG DQAAA----
SELENOP-002 | 缺失Ex5: Sec位点-2
多序列比对说明: SELENOP-001含10个Sec(UGA)位点,SELENOP-002缺失外显子5导致Sec位点减少2个